Nat Med | အူမကြီးကင်ဆာ၏ ပေါင်းစပ်အကျိတ်၊ ကိုယ်ခံအားနှင့် အဏုဇီဝဗေဒဆိုင်ရာ ရှုခင်းကို မြေပုံရေးဆွဲရန် multi-omics ချဉ်းကပ်မှုသည် အဏုဇီဝဗေဒနှင့် ကိုယ်ခံအားစနစ် အပြန်အလှန် ဆက်စပ်မှုကို ဖော်ပြသည်။
မကြာသေးမီနှစ်များအတွင်း မူလအူမကြီးကင်ဆာအတွက် ဇီဝအမှတ်အသားများကို ကျယ်ကျယ်ပြန့်ပြန့် လေ့လာခဲ့သော်လည်း၊ လက်ရှိဆေးခန်းလမ်းညွှန်ချက်များသည် ကုသမှုအကြံပြုချက်များကို ဆုံးဖြတ်ရန်အတွက် အကျိတ်-ပြန်ရည်ကျိတ်-ပြန့်ပွားမှု အဆင့်သတ်မှတ်ခြင်းနှင့် DNA mismatch repair (MMR) ချို့ယွင်းချက်များ သို့မဟုတ် microsatellite instability (MSI) ကို ရှာဖွေခြင်း (စံရောဂါဗေဒစစ်ဆေးမှုအပြင်) ကိုသာ အားကိုးနေရသည်။ သုတေသီများက Cancer Genome Atlas (TCGA) အူမကြီးကင်ဆာ cohort တွင် gene expression-based immune responses၊ microbial profiles နှင့် tumor stroma နှင့် လူနာရှင်သန်မှုတို့အကြား ဆက်စပ်မှုမရှိခြင်းကို ထောက်ပြခဲ့ကြသည်။
သုတေသနတိုးတက်လာသည်နှင့်အမျှ ကင်ဆာ၏ ကင်ဆာဆဲလ်၊ ကိုယ်ခံအား၊ stromal သို့မဟုတ် အဏုဇီဝသဘောသဘာဝ အပါအဝင် မူလအူမကြီးကင်ဆာ၏ အရေအတွက်ဆိုင်ရာ ဝိသေသလက္ခဏာများသည် လက်တွေ့ရလဒ်များနှင့် သိသိသာသာ ဆက်စပ်နေကြောင်း သတင်းပို့ထားသော်လည်း ၎င်းတို့၏ အပြန်အလှန် ဆက်သွယ်မှုများသည် လူနာရလဒ်များကို မည်သို့အကျိုးသက်ရောက်သည်ကို နားလည်မှု အကန့်အသတ်ရှိနေဆဲဖြစ်သည်။
ဖီနိုတိုက်ပစ်ရှုပ်ထွေးမှုနှင့် ရလဒ်အကြား ဆက်နွယ်မှုကို ခွဲခြမ်းစိတ်ဖြာရန်အတွက်၊ ကာတာနိုင်ငံရှိ Sidra Institute of Medical Research မှ သုတေသီအဖွဲ့တစ်ဖွဲ့သည် မကြာသေးမီက microbiome ဝိသေသလက္ခဏာများနှင့် immune rejection constants (ICR) ကို ပေါင်းစပ်ခြင်းဖြင့် ရှင်သန်နှုန်းကောင်းမွန်သော လူနာအုပ်စုတစ်စုကို ဖော်ထုတ်သည့် integrated score (mICRoScore) ကို တီထွင်ပြီး အတည်ပြုခဲ့သည်။ အဖွဲ့သည် primary colorectal cancer ရှိသူ ၃၄၈ ဦးထံမှ လတ်ဆတ်သော frozen နမူနာများကို ပြည့်စုံသော genomic analysis ပြုလုပ်ခဲ့ပြီး၊ ၎င်းတွင် tumor များ၏ RNA sequencing နှင့် ကျန်းမာသော colorectal တစ်ရှူး၊ whole exome sequencing၊ deep T-cell receptor နှင့် 16S bacterial rRNA gene sequencing တို့ ပါဝင်ပြီး microbiome ကို ပိုမိုသွင်ပြင်လက္ခဏာဖော်ပြရန် whole tumor genome sequencing ဖြင့် ဖြည့်စွက်ထားသည်။ ဤလေ့လာမှုကို Nature Medicine တွင် “An integrated tumor, immune and microbiome atlas of colon cancer” အဖြစ် ထုတ်ဝေခဲ့သည်။

Nature Medicine မှာ ထုတ်ဝေတဲ့ ဆောင်းပါး
AC-ICAM ခြုံငုံသုံးသပ်ချက်
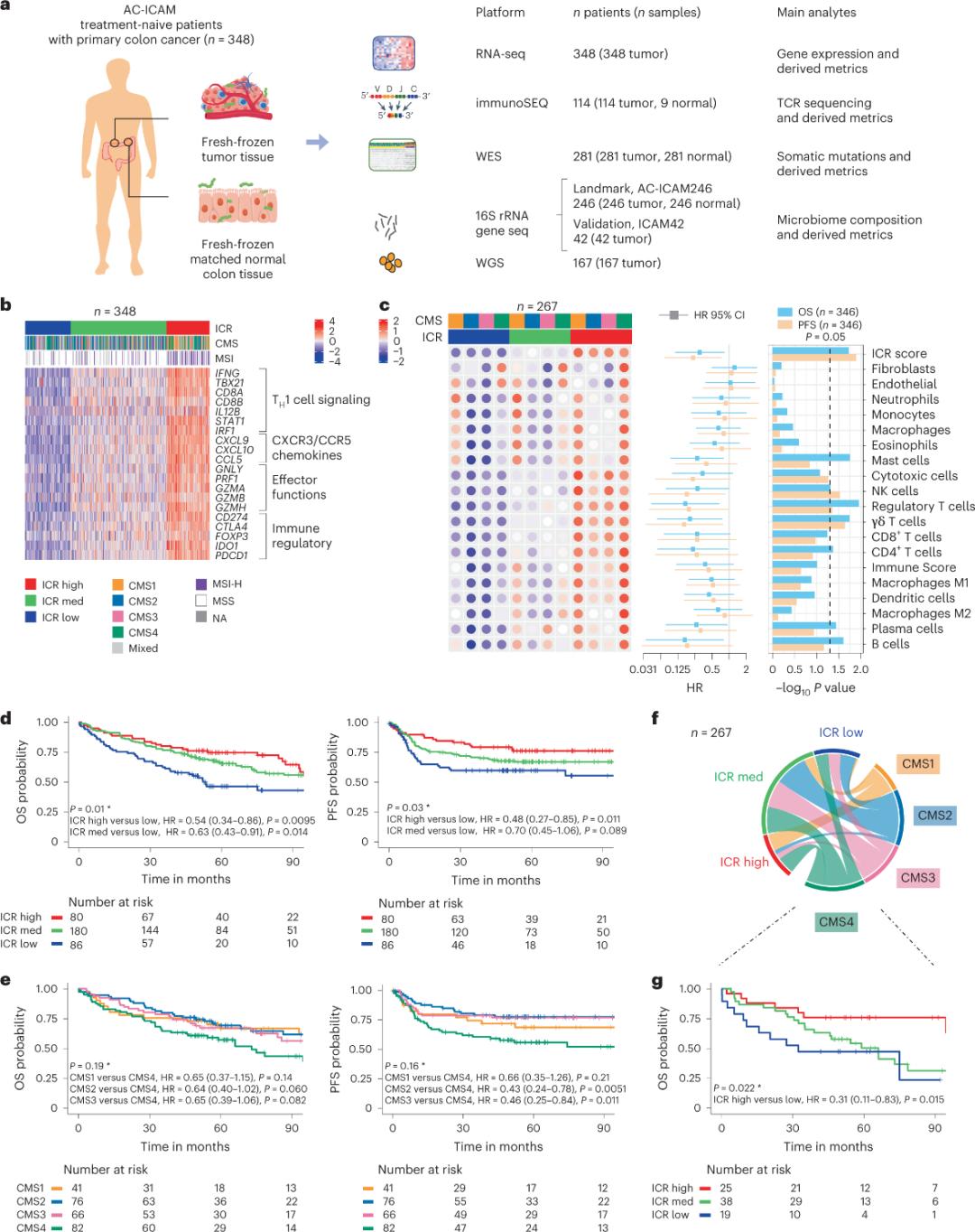
သုတေသီများသည် လတ်ဆတ်သော အေးခဲထားသော အကျိတ်နမူနာများကို ခွဲခြမ်းစိတ်ဖြာရန်နှင့် စနစ်တကျကုထုံးမရှိဘဲ အူမကြီးကင်ဆာရောဂါရှာဖွေတွေ့ရှိထားသော လူနာများထံမှ ကပ်လျက်ကျန်းမာသော အူမကြီးတစ်ရှူး (အကျိတ်-ပုံမှန်အတွဲများ) ကို ကိုက်ညီစေရန်အတွက် orthogonal genomic platform ကို အသုံးပြုခဲ့ကြသည်။ whole-exome sequencing (WES)၊ RNA-seq data quality control နှင့် inclusion criteria screening တို့အပေါ်အခြေခံ၍ လူနာ ၃၄၈ ဦးထံမှ genomic data များကို သိမ်းဆည်းထားပြီး ပျမ်းမျှ follow-up ၄.၆ နှစ်ဖြင့် downstream analysis အတွက် အသုံးပြုခဲ့သည်။ သုတေသနအဖွဲ့သည် ဤအရင်းအမြစ်ကို Sidra-LUMC AC-ICAM: A map and guide to immune-cancer-microbiome interactions (ပုံ ၁) ဟု အမည်ပေးခဲ့သည်။
ICR ကို အသုံးပြု၍ မော်လီကျူးခွဲခြားခြင်း
ကင်ဆာခုခံအား စောင့်ကြည့်ရေးအတွက် ကိုယ်ခံအား မျိုးရိုးဗီဇဆိုင်ရာ အမှတ်အသားများကို အဆက်မပြတ် ဖမ်းယူခြင်းဖြင့်၊ ၎င်းကို immune constant of rejection (ICR) ဟုခေါ်ပြီး၊ သုတေသနအဖွဲ့သည် melanoma၊ ဆီးအိမ်ကင်ဆာနှင့် ရင်သားကင်ဆာ အပါအဝင် မတူညီသော ကင်ဆာအမျိုးအစားများကို လွှမ်းခြုံထားသော မျိုးဗီဇ ၂၀ ပါ panel အဖြစ်သို့ စုစည်းခြင်းဖြင့် ICR ကို အကောင်းဆုံးဖြစ်အောင် ပြုလုပ်ခဲ့သည်။ ICR သည် ရင်သားကင်ဆာ အပါအဝင် ကင်ဆာအမျိုးအစား အမျိုးမျိုးတွင် ကိုယ်ခံအား ကုထုံး တုံ့ပြန်မှုနှင့်လည်း ဆက်စပ်နေသည်။
ပထမဦးစွာ သုတေသီများသည် AC-ICAM cohort ၏ ICR လက်မှတ်ကို အတည်ပြုခဲ့ပြီး၊ cohort ကို clusters/immune subtypes သုံးမျိုးခွဲခြားရန် ICR gene-based co-classification ချဉ်းကပ်မှုကို အသုံးပြုခဲ့သည်- မြင့်မားသော ICR (အပူအကျိတ်များ)၊ အလယ်အလတ် ICR နှင့် နိမ့်သော ICR (အအေးအကျိတ်များ) (ပုံ ၁ခ)။ သုတေသီများသည် အူမကြီးကင်ဆာ၏ transcriptome-based classification တစ်ခုဖြစ်သည့် consensus molecular subtypes (CMS) နှင့် ဆက်စပ်နေသော immune pathogen ကို သွင်ပြင်လက္ခဏာပြခဲ့သည်။ CMS အမျိုးအစားများတွင် CMS1/immune၊ CMS2/canonical၊ CMS3/metabolic နှင့် CMS4/mesenchymal တို့ ပါဝင်သည်။ ICR ရမှတ်များသည် CMS subtypes အားလုံးရှိ အချို့သော ကင်ဆာဆဲလ်လမ်းကြောင်းများနှင့် အနုတ်လက္ခဏာဆက်စပ်နေပြီး immunosuppressive နှင့် stromal-related လမ်းကြောင်းများနှင့် အပြုသဘောဆက်စပ်မှုများကို CMS4 အကျိတ်များတွင်သာ တွေ့ရှိရသည်။
CMS အားလုံးတွင် သဘာဝသတ်ဖြတ်သူ (NK) ဆဲလ်နှင့် T ဆဲလ်အုပ်စုငယ်များ၏ ပေါများမှုသည် ICR မြင့်မားသော ကိုယ်ခံအားမျိုးကွဲများတွင် အများဆုံးဖြစ်ပြီး အခြားသွေးဖြူဥအုပ်စုငယ်များတွင် ပိုမိုကွဲပြားမှုရှိသည် (ပုံ ၁ဂ)။ ICR ကိုယ်ခံအားမျိုးကွဲများတွင် OS နှင့် PFS ကွဲပြားမှုများရှိပြီး ICR တွင် အနိမ့်မှ မြင့်မားသို့ တဖြည်းဖြည်းတိုးလာသည် (ပုံ ၁ဃ)၊ ၎င်းသည် အူမကြီးကင်ဆာတွင် ICR ၏ ရောဂါခန့်မှန်းချက်ဆိုင်ရာ အခန်းကဏ္ဍကို အတည်ပြုပေးသည်။
ပုံ ၁။ AC-ICAM လေ့လာမှုဒီဇိုင်း၊ ကိုယ်ခံအားနှင့်ဆက်စပ်သော မျိုးဗီဇလက္ခဏာများ၊ ကိုယ်ခံအားနှင့် မော်လီကျူးမျိုးကွဲများနှင့် ရှင်သန်မှု။
ICR သည် အကျိတ်ကြွယ်ဝသော၊ ကလိုနရယ်ဖြင့် ချဲ့ထွင်ထားသော T ဆဲလ်များကို ဖမ်းယူသည်
အကျိတ်တစ်ရှူးထဲသို့ စိမ့်ဝင်သော T ဆဲလ်အနည်းငယ်သာ အကျိတ်အင်တီဂျင်များအတွက် တိကျမှုရှိကြောင်း သတင်းပို့ထားသည် (၁၀%)။ ထို့ကြောင့်၊ intra-tumor T ဆဲလ်အများစုကို bystander T ဆဲလ်များ (bystander T ဆဲလ်များ) အဖြစ်ရည်ညွှန်းသည်။ ထုတ်လုပ်နိုင်သော TCR များပါရှိသော ရိုးရာ T ဆဲလ်အရေအတွက်နှင့် အခိုင်မာဆုံးဆက်စပ်မှုကို stromal cell နှင့် leukocyte subpopulations (RNA-seq မှတွေ့ရှိသည်) တွင် တွေ့ရှိခဲ့ပြီး၊ ၎င်းတို့ကို T cell subpopulations ကို ခန့်မှန်းရန်အသုံးပြုနိုင်သည် (ပုံ ၂က)။ ICR clusters (အလုံးစုံနှင့် CMS အမျိုးအစားခွဲခြားမှု) တွင်၊ immune SEQ TCR များ၏ အမြင့်ဆုံး clonality ကို ICR-high နှင့် CMS subtype CMS1/immune အုပ်စုများ (ပုံ ၂ဂ) တွင် တွေ့ရှိခဲ့ပြီး၊ ICR-high အကျိတ်များ၏ အချိုးအစား အမြင့်ဆုံးဖြစ်သည်။ transcriptome တစ်ခုလုံး (ဂျင်း ၁၈,၂၇၀) ကို အသုံးပြုခြင်းဖြင့်၊ ICR ဂျင်းခြောက်ခု (IFNG၊ STAT1၊ IRF1၊ CCL5၊ GZMA နှင့် CXCL10) သည် TCR immune SEQ clonality နှင့် အပြုသဘောဆောင်သော ဆက်စပ်နေသော ဂျင်းဆယ်မျိုးတွင် ပါဝင်သည် (ပုံ ၂ဃ)။ ImmunoSEQ TCR clonality သည် tumor-responsive CD8+ markers များကို အသုံးပြု၍ တွေ့ရှိရသည့် correlations များထက် ICR gene အများစုနှင့် ပိုမိုခိုင်မာစွာ ဆက်စပ်နေသည် (ပုံ 2f နှင့် 2g)။ အဆုံးသတ်အနေဖြင့်၊ အထက်ဖော်ပြပါ ခွဲခြမ်းစိတ်ဖြာမှုက ICR signature သည် tumor-riched, clonally amplified T cells များရှိနေခြင်းကို ဖမ်းယူထားပြီး ၎င်း၏ ရောဂါခန့်မှန်းချက်ဆိုင်ရာ သက်ရောက်မှုများကို ရှင်းပြနိုင်သည်ဟု အကြံပြုထားသည်။
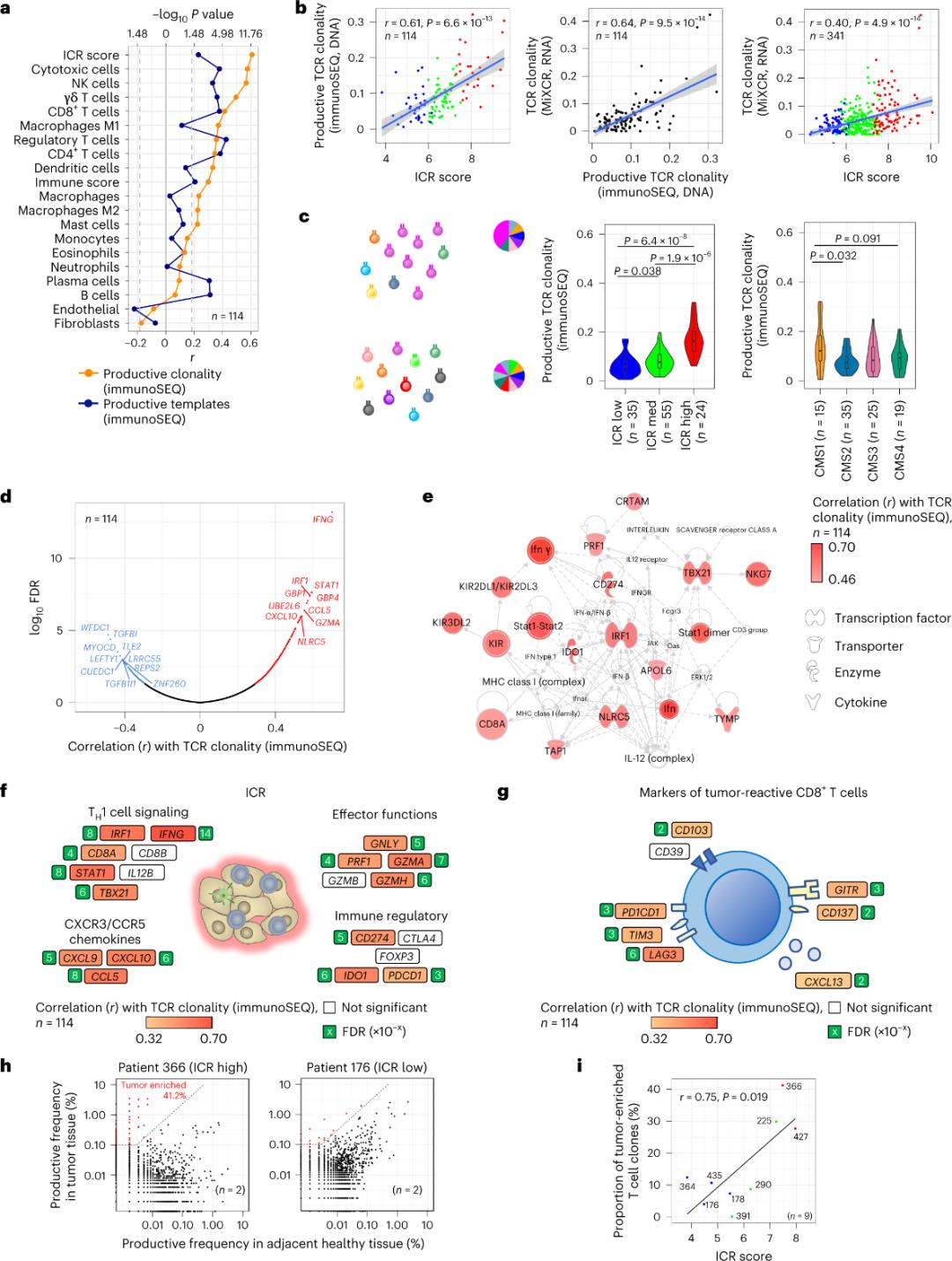
ပုံ ၂။ TCR မက်ထရစ်များနှင့် ကိုယ်ခံအားနှင့်ဆက်စပ်သော မျိုးဗီဇများ၊ ကိုယ်ခံအားနှင့် မော်လီကျူးမျိုးကွဲများနှင့် ဆက်စပ်မှု။
ကျန်းမာသောနှင့် အူမကြီးကင်ဆာတစ်ရှူးများရှိ အဏုဇီဝဖွဲ့စည်းမှု
သုတေသီများသည် လူနာ ၂၄၆ ဦးထံမှ ကိုက်ညီသော အကျိတ်နှင့် ကျန်းမာသော အူမကြီးတစ်ရှူးမှ ထုတ်ယူထားသော DNA ကို အသုံးပြု၍ 16S rRNA sequencing ကို ပြုလုပ်ခဲ့သည် (ပုံ ၃က)။ အတည်ပြုရန်အတွက် သုတေသီများသည် ခွဲခြမ်းစိတ်ဖြာရန် ရရှိနိုင်သော ပုံမှန် DNA နှင့် ကိုက်ညီမှုမရှိသော နောက်ထပ် အကျိတ်နမူနာ ၄၂ ခုမှ 16S rRNA gene sequencing အချက်အလက်များကို ထပ်မံခွဲခြမ်းစိတ်ဖြာခဲ့ကြသည်။ ပထမဦးစွာ သုတေသီများသည် ကိုက်ညီသော အကျိတ်များနှင့် ကျန်းမာသော အူမကြီးတစ်ရှူးများအကြားရှိ flora များ၏ နှိုင်းရပေါများမှုကို နှိုင်းယှဉ်ခဲ့ကြသည်။ ကျန်းမာသော နမူနာများနှင့် နှိုင်းယှဉ်ပါက အကျိတ်များတွင် Clostridium perfringens သိသိသာသာ တိုးလာသည် (ပုံ ၃က-၃ဃ)။ အကျိတ်နှင့် ကျန်းမာသော နမူနာများအကြား alpha diversity (နမူနာတစ်ခုတည်းတွင် မျိုးစိတ်များ ကွဲပြားမှုနှင့် ပေါများမှု) တွင် သိသာထင်ရှားသော ကွာခြားချက်မရှိခဲ့ဘဲ ICR-low အကျိတ်များနှင့် နှိုင်းယှဉ်ပါက ICR-high အကျိတ်များတွင် microbial diversity အနည်းငယ် လျော့ကျသွားသည်ကို တွေ့ရှိခဲ့ရသည်။
အဏုဇီဝပရိုဖိုင်များနှင့် ဆေးခန်းရလဒ်များအကြား ဆေးခန်းဆိုင်ရာ သက်ဆိုင်ရာဆက်စပ်မှုများကို ထောက်လှမ်းရန်အတွက် သုတေသီများသည် ရှင်သန်မှုကို ခန့်မှန်းသည့် အဏုဇီဝဇီဝအင်္ဂါရပ်များကို ဖော်ထုတ်ရန် 16S rRNA မျိုးဗီဇအစီအစဉ်ဒေတာကို အသုံးပြုရန် ရည်ရွယ်ခဲ့သည်။ AC-ICAM246 တွင် သုတေသီများသည် MBR အမျိုးအစားခွဲခြားသူများဟုခေါ်သော သုညမဟုတ်သော ကိန်းဂဏန်းများ (သေဆုံးမှုနှုန်းကွဲပြားမှုနှင့် ဆက်စပ်နေ) ရှိသော အင်္ဂါရပ် ၄၁ ခုကို ရွေးချယ်သည့် OS Cox regression မော်ဒယ်ကို လုပ်ဆောင်ခဲ့သည် (ပုံ ၃f)။
ဤလေ့ကျင့်ရေး cohort (ICAM246) တွင် MBR ရမှတ်နိမ့်ခြင်း (MBR<0၊ MBR နိမ့်ခြင်း) သည် သေဆုံးနိုင်ခြေ သိသိသာသာ နည်းပါးခြင်း (85%) နှင့် ဆက်စပ်နေပါသည်။ သုတေသီများသည် သီးခြားစီ အတည်ပြုထားသော cohorts နှစ်ခု (ICAM42 နှင့် TCGA-COAD) တွင် MBR နိမ့်ခြင်း (အန္တရာယ်) နှင့် ကြာရှည်သော OS အကြား ဆက်စပ်မှုကို အတည်ပြုခဲ့သည်။ (ပုံ ၃) လေ့လာမှုတွင် endogastric cocci နှင့် MBR ရမှတ်များအကြား ခိုင်မာသော ဆက်စပ်မှုကို ပြသခဲ့ပြီး ၎င်းတို့သည် အကျိတ်နှင့် ကျန်းမာသော အူမကြီးတစ်ရှူးတွင် အလားတူဖြစ်သည်။
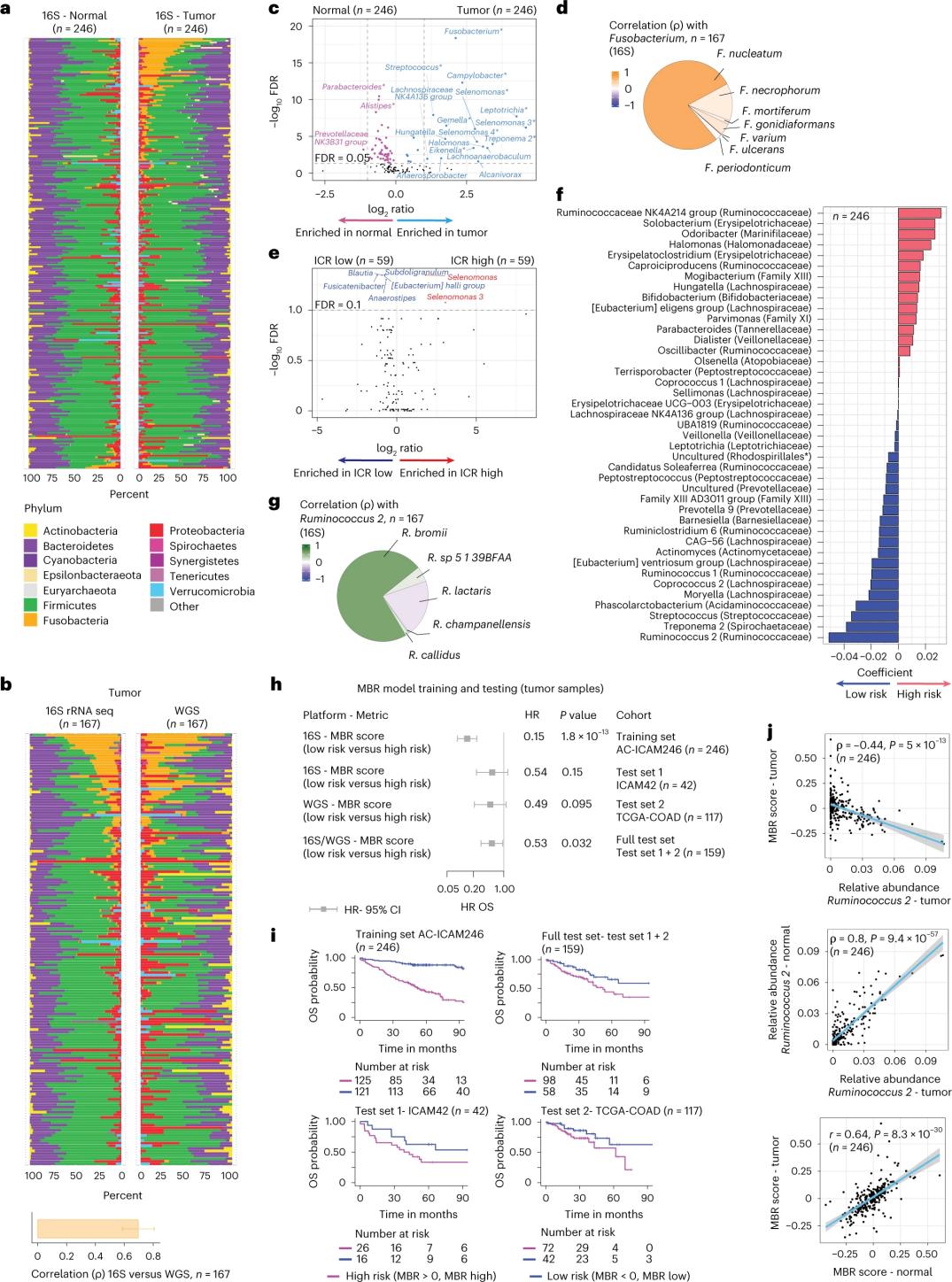
ပုံ ၃။ အကျိတ်နှင့် ကျန်းမာသောတစ်ရှူးများရှိ အဏုဇီဝပိုးမွှားများနှင့် ICR နှင့် လူနာရှင်သန်မှုနှင့် ဆက်နွယ်မှု။
နိဂုံးချုပ်
ဤလေ့လာမှုတွင်အသုံးပြုသော multi-omics ချဉ်းကပ်မှုသည် အူမကြီးကင်ဆာတွင် ကိုယ်ခံအားတုံ့ပြန်မှု၏ မော်လီကျူးလက္ခဏာကို သေချာစွာ ထောက်လှမ်းခြင်းနှင့် ခွဲခြမ်းစိတ်ဖြာခြင်းကို ပြုလုပ်နိုင်စေပြီး အဏုဇီဝပိုးမွှားနှင့် ကိုယ်ခံအားစနစ်အကြား အပြန်အလှန် ဆက်သွယ်မှုကိုလည်း ဖော်ထုတ်ပေးပါသည်။ အကျိတ်နှင့် ကျန်းမာသောတစ်ရှူးများ၏ နက်ရှိုင်းသော TCR အစီအစဉ်က ICR ၏ ခန့်မှန်းချက်အကျိုးသက်ရောက်မှုသည် အကျိတ်ကြွယ်ဝပြီး အကျိတ်အင်တီဂျင်-သီးသန့် T ဆဲလ်ကလုန်းများကို ဖမ်းယူနိုင်စွမ်းကြောင့် ဖြစ်နိုင်ကြောင်း ဖော်ပြသည်။
AC-ICAM နမူနာများတွင် 16S rRNA မျိုးဗီဇ အစီအစဉ်ရှာဖွေခြင်းကို အသုံးပြု၍ အကျိတ် အဏုဇီဝဖွဲ့စည်းပုံကို ခွဲခြမ်းစိတ်ဖြာခြင်းဖြင့် အဖွဲ့သည် ခန့်မှန်းချက်တန်ဖိုး မြင့်မားသော အဏုဇီဝလက္ခဏာ (MBR အန္တရာယ်ရမှတ်) ကို ဖော်ထုတ်ခဲ့သည်။ ဤလက်မှတ်ကို အကျိတ်နမူနာများမှ ရရှိသော်လည်း၊ ကျန်းမာသော အူမကြီးနှင့် အကျိတ် MBR အန္တရာယ်ရမှတ်အကြား ခိုင်မာသော ဆက်စပ်မှုရှိပြီး ဤလက်မှတ်သည် လူနာများ၏ အူလမ်းကြောင်း အဏုဇီဝဖွဲ့စည်းပုံကို ဖမ်းယူနိုင်ကြောင်း အကြံပြုထားသည်။ ICR နှင့် MBR ရမှတ်များကို ပေါင်းစပ်ခြင်းဖြင့် အူမကြီးကင်ဆာရှိသော လူနာများတွင် ရှင်သန်နိုင်ခြေကို ခန့်မှန်းသည့် multi-omic ကျောင်းသား ဇီဝအမှတ်အသားကို ဖော်ထုတ်ပြီး အတည်ပြုနိုင်ခဲ့သည်။ လေ့လာမှု၏ multi-omic dataset သည် အူမကြီးကင်ဆာဇီဝဗေဒကို ပိုမိုနားလည်ရန်နှင့် ကိုယ်ပိုင်ကုထုံးနည်းလမ်းများကို ရှာဖွေတွေ့ရှိရန် အရင်းအမြစ်တစ်ခုကို ပံ့ပိုးပေးပါသည်။
ပို့စ်တင်ချိန်: ၂၀၂၃ ခုနှစ်၊ ဇွန်လ ၁၅ ရက်
 中文网站
中文网站